ポイント
- 酵素[用語1]活性を指標とした世界最小スケールかつ最速の酵素開発技術を発明。
- 酵素とその遺伝情報(mRNA)1分子複合体を形成させ、活性ある酵素分子をその遺伝子とともに取得可能。
- 環境負荷の低い酵素プロセスや、バイオセンサーなどの有用酵素開発を加速。
概要
酵素は食品や洗剤をはじめ、医薬品や化学製品、燃料などの製造に多く使われており、環境負荷の低い触媒としてその利用範囲は世界的に増大しています。
東京科学大学(Science Tokyo) 総合研究院 化学生命科学研究所の北口哲也准教授、シュ・ハク(朱博) 助教は、名古屋大学 大学院生命農学研究科のダムナニョヴィッチ・ ヤスミナ(Damnjanovic Jasmina)准教授、中野秀雄教授、ムナウィーラ・カルハリ(Munaweera Kalhari)博士後期課程学生、カマーニャ・マウリツィオ(Canagna Maurizio)博士、伊藤智和准教授らの研究グループ、埼玉大学 大学院理工学研究科の根本直人特任教授と共同で、産業的に有用な酵素の1分子スクリーニングを可能にする新規な酵素選択システムSMART法を開発しました。
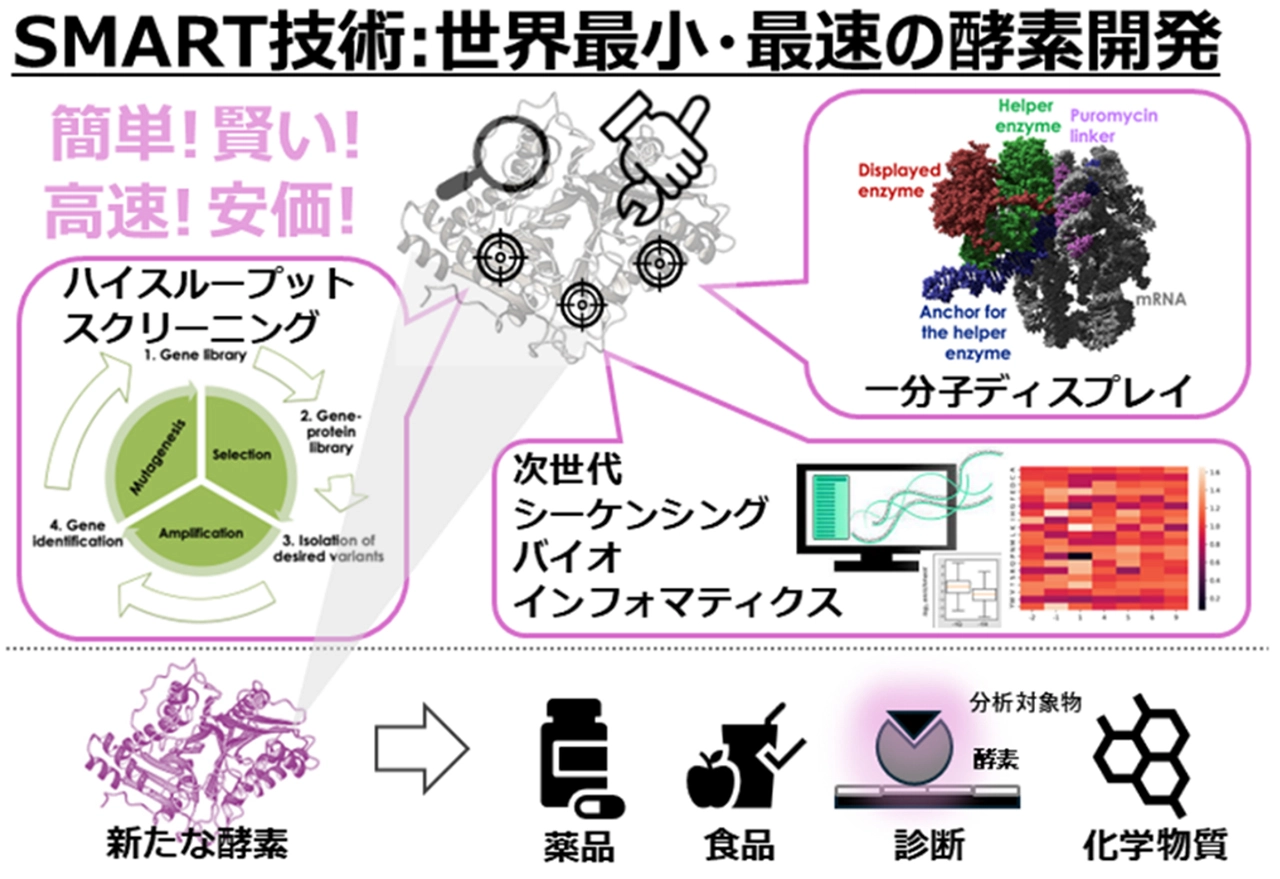
このシステムの特徴は設計図(mRNA)と製品(酵素・タンパク質)、さらにこの標的酵素反応に応じて目印をつけるヘルパー酵素を1分子レベルでセットにすることです。通常、酵素などタンパク質を作ると設計図から離れてしまいますが、この技術では「設計図」と「製品」を強力な糊でくっつけたままにします。そのため、膨大な標的酵素変異体のうち、活性を有する標的酵素分子が含まれる複合体だけにヘルパー酵素の作用により目印がつけられることで、その遺伝子までもが一緒に"釣れる"のです。同様の技術はこれまで特定の分子に結合するペプチドや抗体で開発され、実用化されていました。本研究では酵素、しかも産業用有用な酵素酸化還元反応を行う酵素に対して、その酵素活性を指標とした世界最小で最速の「酵素分子選択システム」を世界で初めて開発しました。
本研究成果により、産業的に「優れた性質をもつ有用酵素」が従来の手法より短時間・低コストで開発可能になると期待されます。このヘルパー酵素は、さまざまな産業用酵素に応用可能であり、食品、医薬、診断薬さらには、化学産業における酵素利用を拡大することが期待されます。
本研究成果は、雑誌『ACS Synthetic Biology 』のASAPに2026年2月23日にオンライン公開されました。正式版は4月に掲載予定です。
背景
生き物は長い年月をかけて、環境に合うように少しずつ形や機能を変えてきました。これを「進化」と呼びますが、自然界では何万年もかかります。一方で2018年のノーベル化学賞の対象になった「指向性進化工学」は、この「進化」のプロセスを実験室で高速に行う技術です。人間にとって便利な「スーパー酵素(特殊な働きをするタンパク質)」を作るために、あえて人工的に「突然変異」を起こし、その中から優秀なものだけを選び抜きます。
自然界にある酵素は、もともと「生き物が生きるため」に最適化されています。しかし、私たちが薬を作ったり、環境に優しい洗剤を作ったりする際には、もっと「熱に強い」「特定の物質だけに反応する」といった、自然界にはない特殊な能力が必要になります。
ここで大きな課題があります。人工的に突然変異させると、候補となるタンパク質のライブラリーの種類は100兆個という、天文学的な数になってしまいます。これら膨大な候補酵素から効率的に見つけ出す手法は、これまでも多数存在し、代表的なものとしては1個の微生物の中や表面に酵素を提示させて選抜する手法です。この場合には微生物への遺伝子の導入が必要になることと、微生物の大きさは1µmから10µmであることから、作ることのできるライブラリーの種類はせいぜい1億個程度でした。
これまでに遺伝子1個と酵素タンパク質1個を結合させる技術はmRNAディスプレイ[用語2]と呼ばれすでに実用化されていました。例えば大学発ベンチャー会社として名高いペプチドリーム社は、このシステムを使って、ペプチド創薬に取り組んでいます。今回さらにヘルパー酵素一個を物理的に近い位置に配置することにより、原理的に世界最大の酵素ライブラリーを世界最小スケールで選抜可能になりました。この独自システムをSMART(Single-Molecule Assay on Ribonucleic acid by Translated product)と名付けています。
研究成果
今回のプロジェクトでは、このSMART技術に「次世代シーケンサー(大量のDNAを超高速で読み取る装置)」と「バイオインフォマティクス」を組み合わせています。これにより「どの設計図が、なぜ優秀だったのか」という膨大なデータをAIなどで解析し、より効率的に、より高性能な酵素を生み出す「プラットフォーム(基盤)」を作ることができました。本成果により、将来的に医薬品合成、バイオセンサーに有用な酵素の創出などに応用されることが期待されます。
付記
本研究は、主に、科学研究費助成事業の若手研究、学術変革領域研究(A)「タンパク質新機能生成」、文部科学省(MEXT)の「物質・デバイス領域共同研究拠点」による共同研究プログラム、および文部科学省「ダイバーシティ研究環境実現イニシアティブ(女性リーダー育成型)」に基づく名古屋大学「女性研究者採用・育成・登用加速プログラム」(Damnjanovic Jasmina氏への授与)の支援を受けました。
用語説明
- [用語1]
- 酵素:遺伝子の配列に従ってつくられるタンパク質分子のうち、化学反応を触媒する分子の総称。食品、医薬品、洗剤など多方面で実用化されている。
- [用語2]
- mRNAディスプレイ:タンパク質はDNAから成る遺伝子からmRNAが転写され、そのmRNAを鋳型としてリボソームによりタンパク質が合成される。特殊なリンカー分子をこのmRNAに結合させることにより、mRNAとタンパク質を1対1で結合できる。この研究では埼玉大学の根本特任教授が開発したリンカーの提供を、根本特任教授が創業した株式会社 Epsilon Molecular Engineering から受けている。
論文情報
- 掲載誌:
- ACS Synthetic Biology
- タイトル:
- Harnessing the Power of SMART Single-Molecule Display for Enzyme Evolution: A Focus on Oxidase
- 著者:
- Munaweera, T. I. K.1, Odake N.1, Halim, H.1, Ikeda, K.1, Zhu, B.2, Camagna, M.1, Ito, T.1, Kitaguchi, T.2, Nemoto, N.3, Nakano, H.1*, Damnjanovic, J.1*
- 所属:
- 1. 名古屋大学
2. 東京科学大学
3. 埼玉大学
関連リンク
お問い合わせ
名古屋大学 大学院生命農学研究科
教授 中野 秀雄
准教授 Damnjanovic Jasmina(ダムナニョヴィッチ・ヤスミナ)
- 備考
- Tel 052-789-4142(中野)、052-789-4168(ヤスミナ)
東京科学大学 総合研究院 化学生命科学研究所
准教授 北口 哲也
- Tel
- 045-924-5270
東京科学大学 総務企画部 広報課
- media@adm.isct.ac.jp
- Tel
- 03-5734-2975
- FAX
- 03-5734-3661